未知反応を触媒する酵素探索
はじめに
事業開発部の礒崎です。弊社では未知反応を担う酵素探索を行っています。既知酵素反応との反応類似度および既知反応を担う酵素配列との配列相同性を基にして、標的の未知反応を担う酵素配列候補を出力します。本ブログでは、その具体例としてエイズ治療薬候補の1つIslatravirという化合物の合成反応を実際に担う酵素配列を予測した結果をご紹介します。
酵素探索に使用した材料
Huffman et al., 2019のデータを使わせていただきました。この論文ではIslatravirの新規合成経路を設計し、経路中の反応それぞれを触媒する酵素を見つけ、その実証実験を行っていました。Islatravirの合成反応を図1に示しました。化合物6 → 化合物7 or 8 → 化合物5 → 化合物4 → 化合物3 + 化合物2 → Islatravirという順番に合成されます。この合成経路の各反応を担う酵素を弊社の酵素探索技術で予測し、論文で使用された酵素と比較しました。

結果
まずは、合成経路の5反応それぞれと類似する反応を探索しました。
1. 類似反応探索
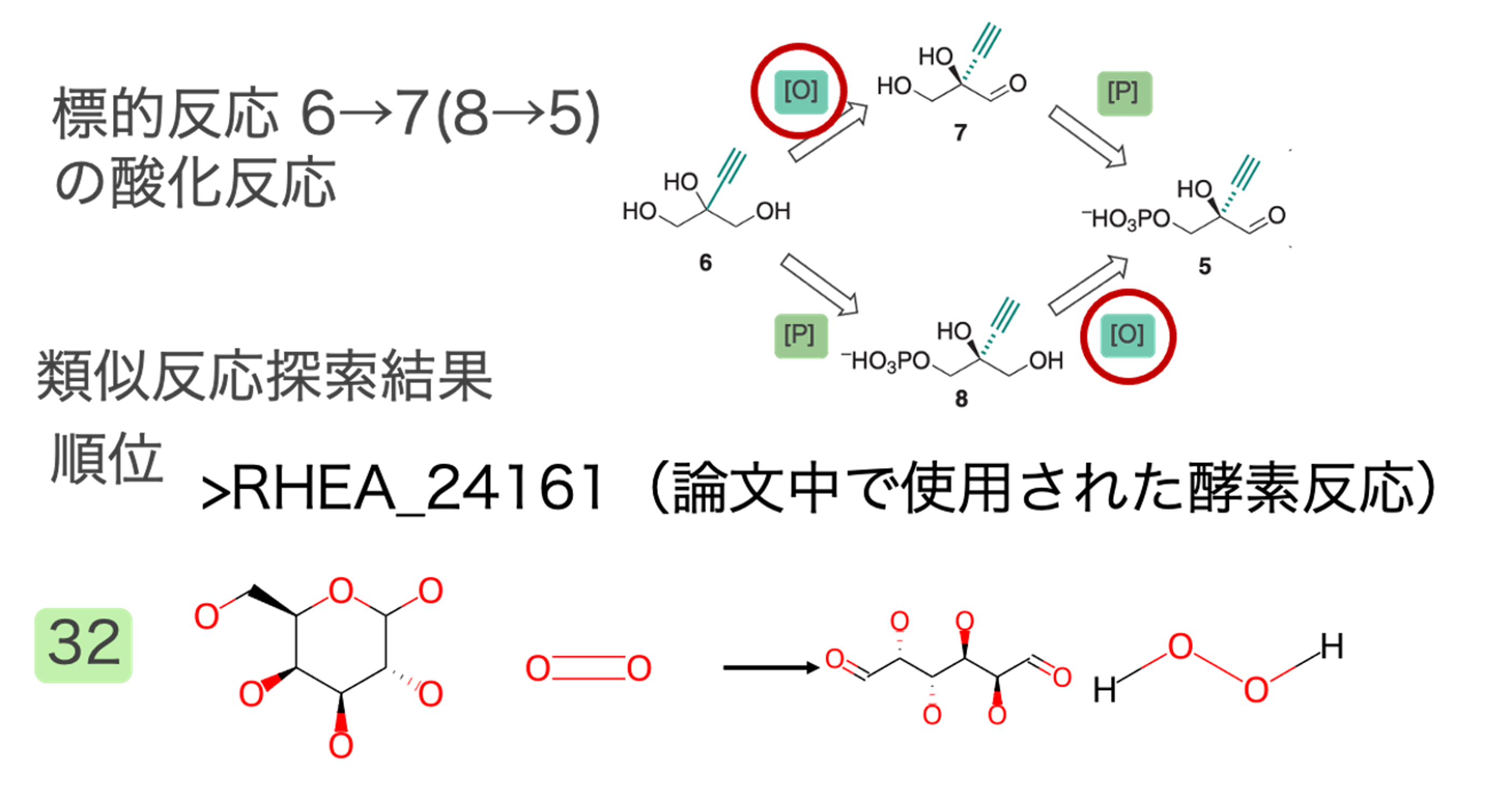
出発物質である6→7 (または8→5)酸化反応の類似反応
水酸基をアルデヒド基に酸化する反応が類似反応として多く抽出されました。標的反応との反応類似度が高い類似反応の一部とその順位を図2に示しました。この反応は既知の代謝反応にはないため複数の類似反応が抽出されました。
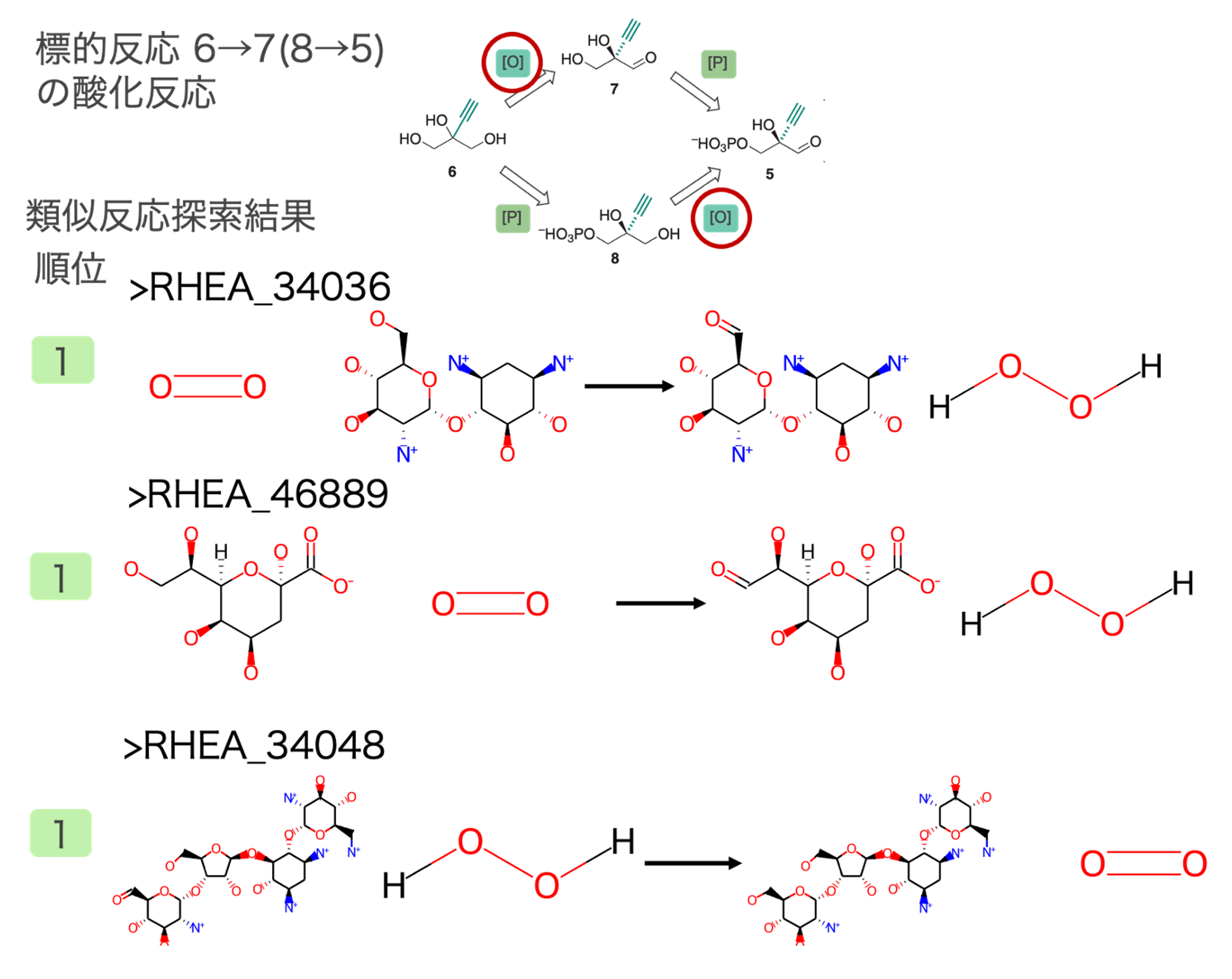
出発物質6→8(または7→5)リン酸化反応の類似反応
水酸基をリン酸化する反応が類似反応として多く抽出されました。標的反応との反応類似度が高い類似反応の一部とその順位を図3に示しました。この反応は上記反応同様、既知の代謝反応にはないため複数候補の類似反応が抽出されました。
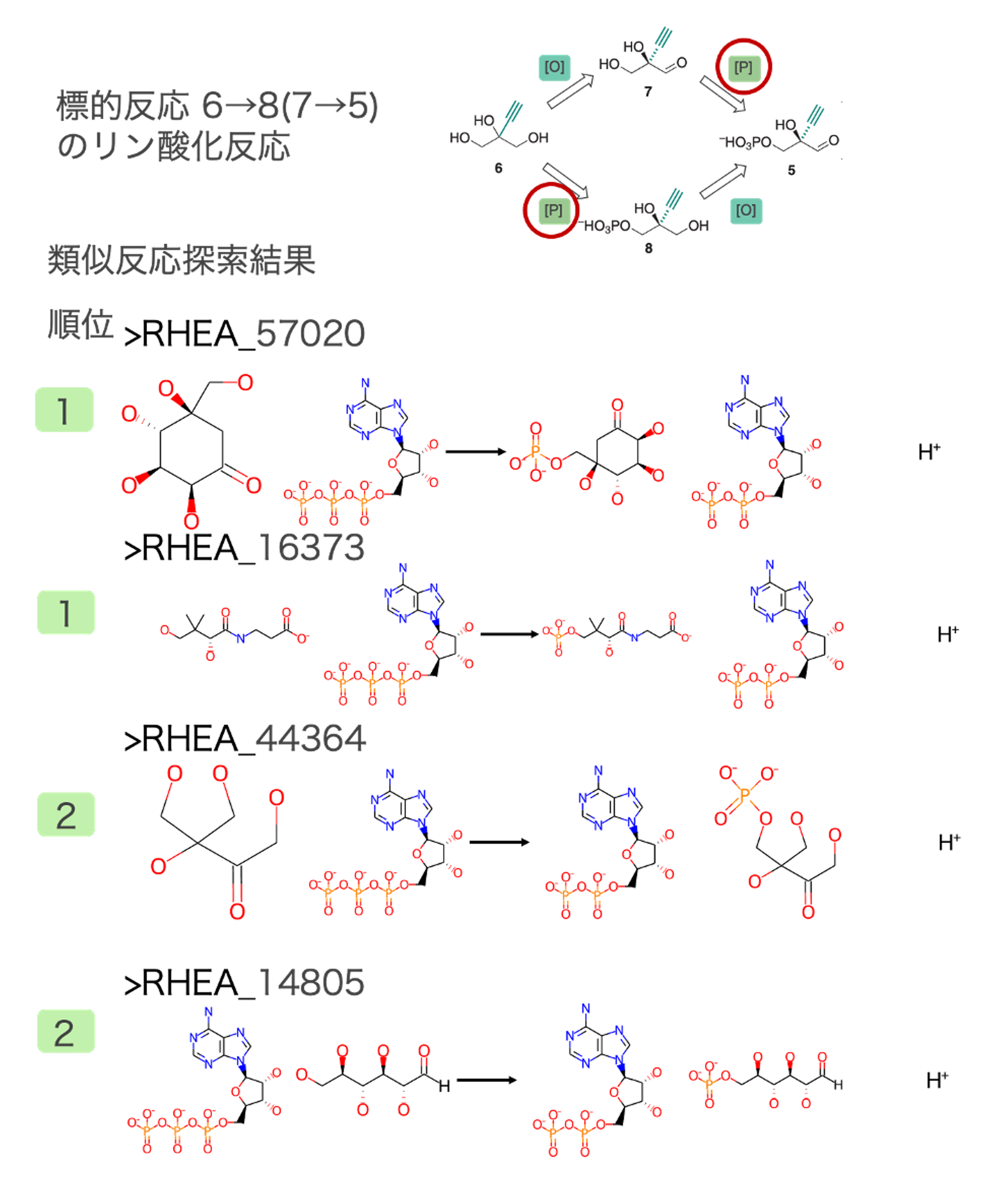
中間体5→4 のリボース合成反応
アセトアルデヒドを添加することで閉環してデオキシリボースとなる反応が抽出されました(図4)。論文中でこの反応は既知の代謝反応を模倣しているため、アルキニル基以外全く同じ反応が類似反応として得られました。
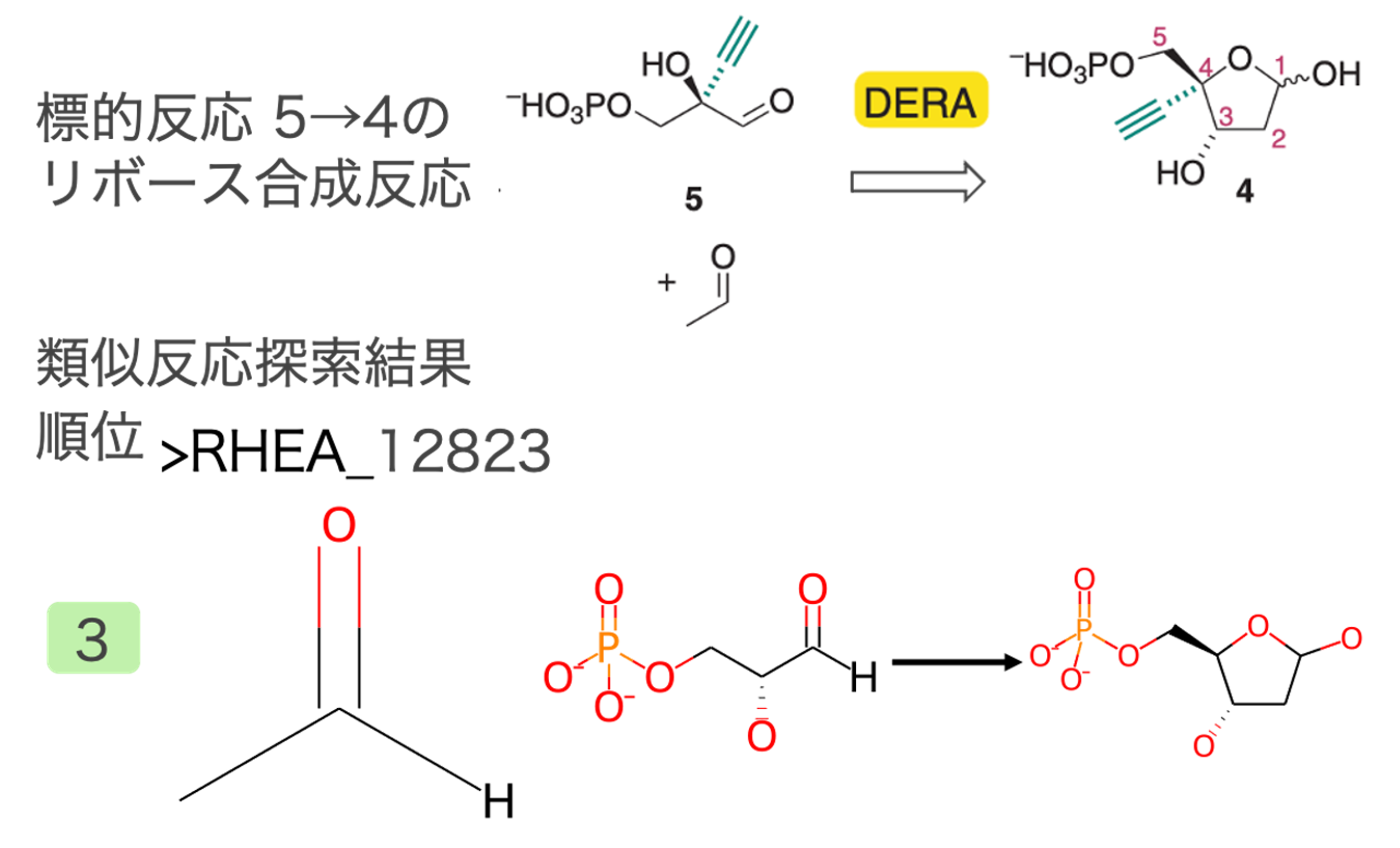
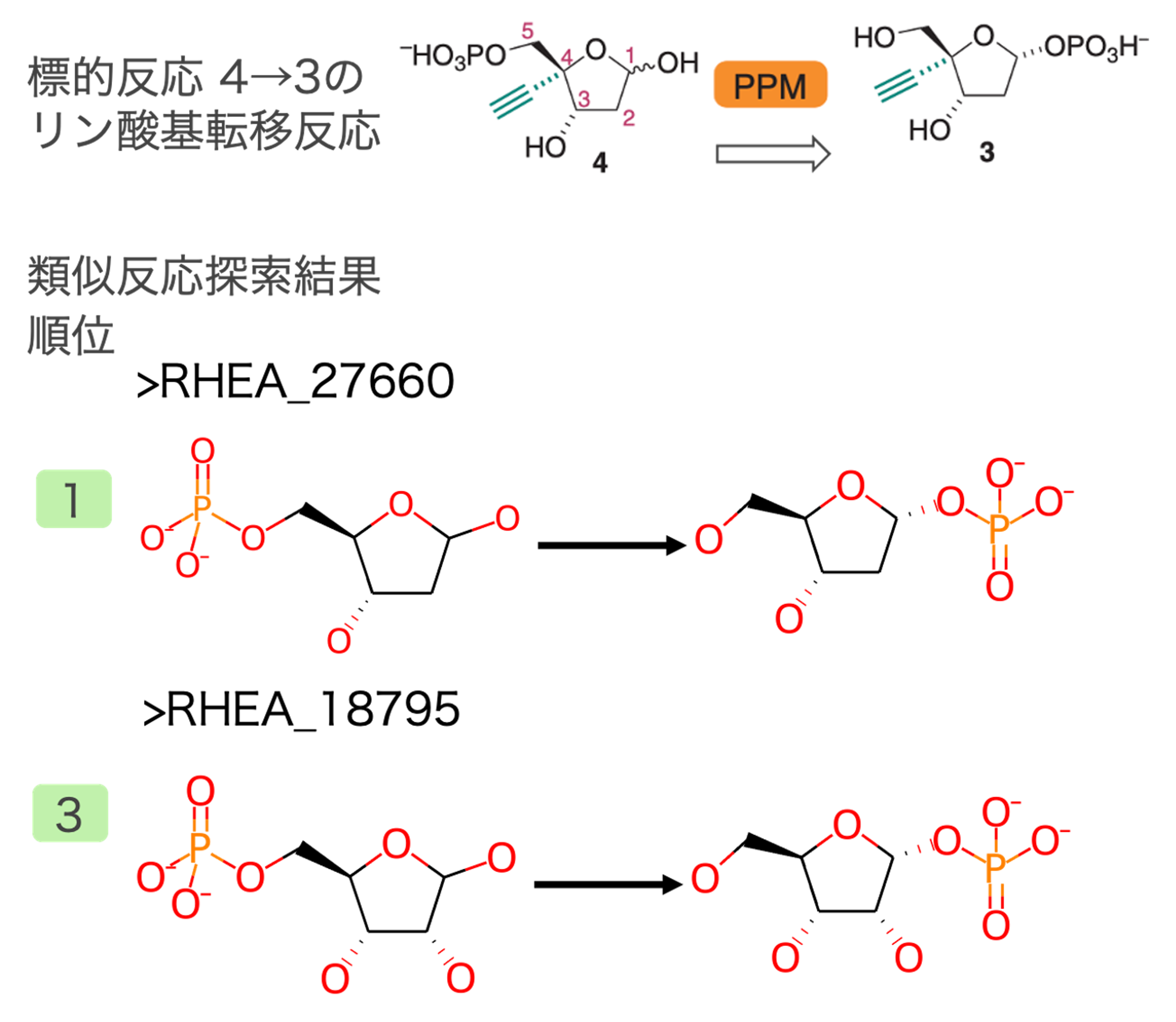
中間体4→3のリン酸基転移反応
リン酸基をヒドロキシアルキル基から水酸基へ転移する反応が抽出されました(図5)。上記リボース合成反応と同様にこの反応も既知の代謝反応を模倣しているため、アルキニル基以外全く同じ反応が類似反応として得られました。
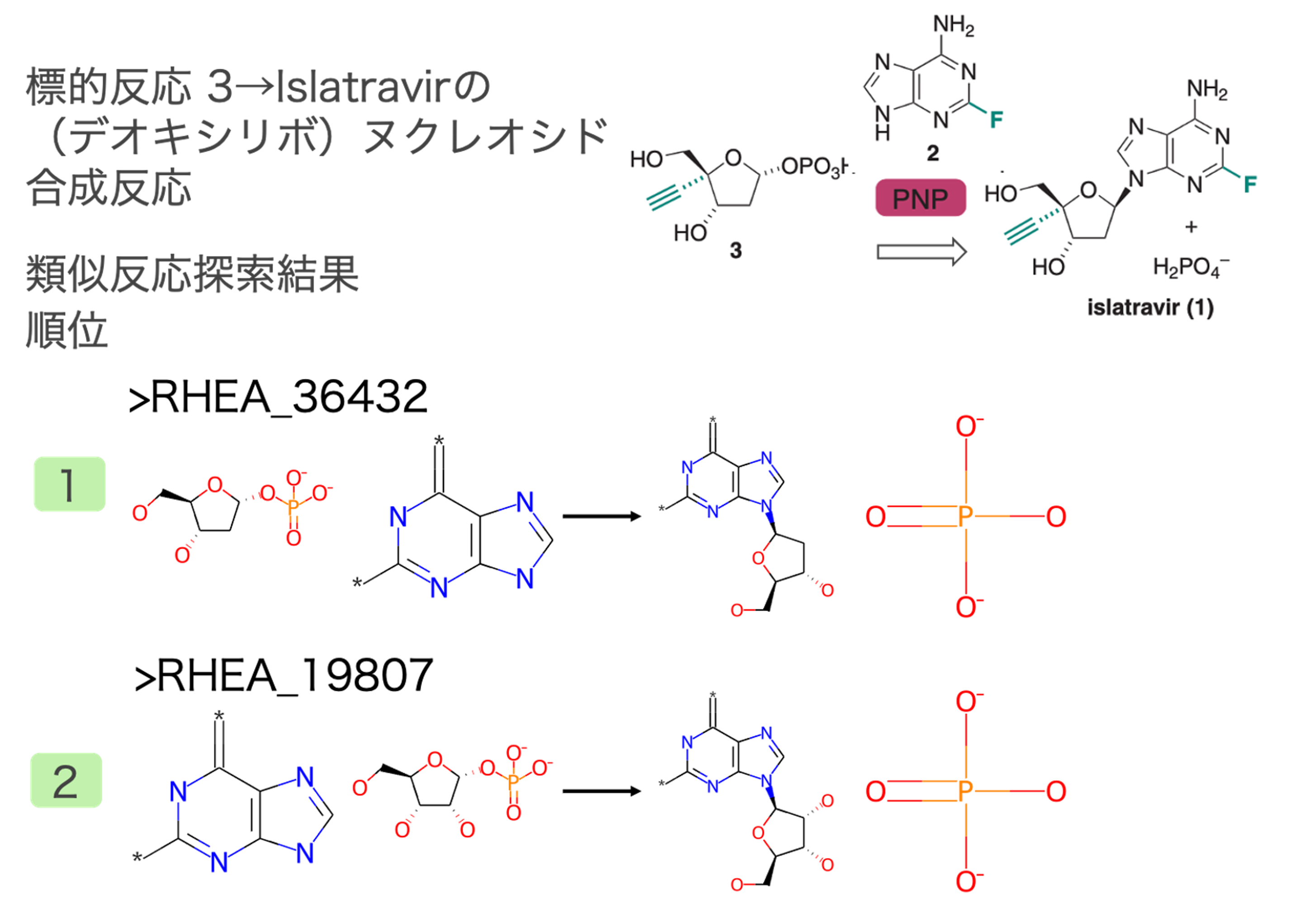
中間体3→Islatravirのヌクレオシド合成反応
プリンをデオキシリボースに付加する反応が抽出されました(図6)。上記リン酸基転移反応と同様にこの反応も既知の代謝反応を模倣しているため、アルキニル基およびフッ素以外全く同じ反応が類似反応として得られました。
2. 類似反応該当酵素探索
結果1で5反応それぞれの類似反応を抽出しました。この類似反応を担う酵素配列をtaxonごとに抽出しました。絞り込んだ配列の中に論文中で使用された酵素が含まれたかを5反応それぞれで調べました。さらに、5反応それぞれにおいて、全taxon由来の酵素配列から系統的位置を用いたスクリーニングにより配列を絞り込みました。
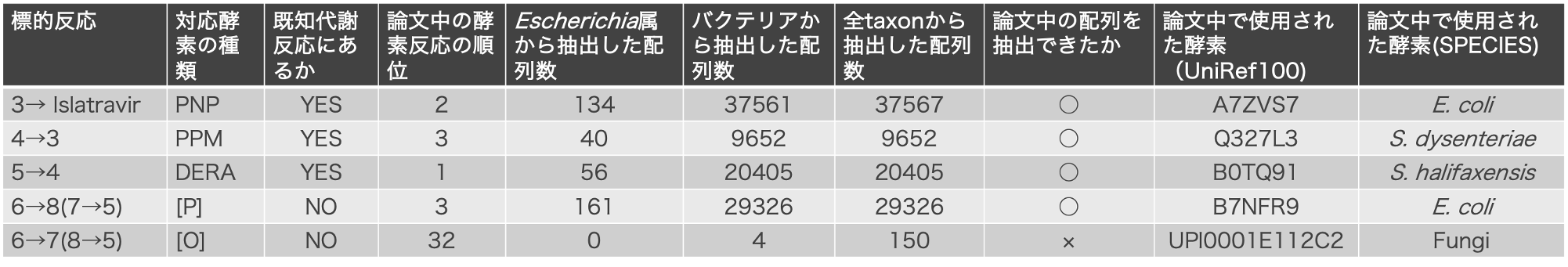
類似反応のTaxonごとの酵素配列抽出
結果1の類似反応を担う酵素を探索し、Escherichia属、バクテリア、全taxon由来の3段階で抽出しました。抽出した配列数を以下の表1に示しました。今回の論文で使用している酵素と一致するものが含まれていたか調べました。5反応中4反応で、弊社酵素探索技術で抽出した酵素配列に論文中で使用された酵素が含まれていました。
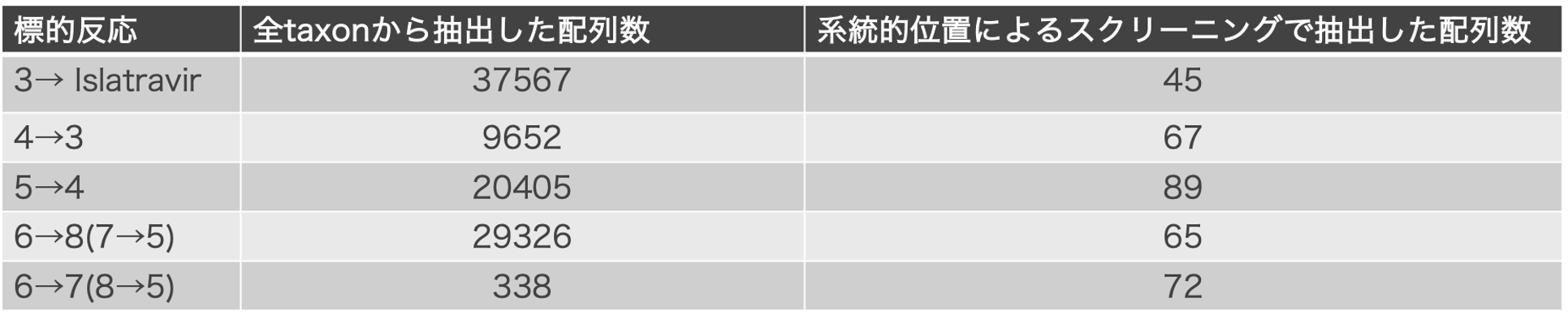
系統的位置によるスクリーニング
全taxonより抽出した上記の類似反応酵素配列から、さらに系統的位置により配列を絞り込みます。全配列をクラスタリング・系統樹を生成、系統的にまとまった配列群から1配列ずつ選定しました。この選定の際、その配列の種間での保存度の高いものを優先して選定します(表2、図7)。

6→7(8→5)の酸化反応についての考察
上記結果にあるように、論文中でこの反応に使用された酵素は今回見つかりませんでした。その要因としては標的反応6→7(8→5)と論文中で使用した酵素反応がそれほど似ていないことにあると考えます(図8)。今回の類似反応探索で見つけた反応も論文中で使用されたO2を利用したOxidoreductaseであり、標的反応を触媒する可能性があると考えます。図9の反応を触媒する酵素として論文中ではUniParc ID: UPI0001E112C2を使用していると推定されます。これはRHEA_24161を触媒することが確認済みの配列のUniRef50のメンバーに含まれています。UPI0001E112C2自体はこの反応を触媒するかcurationされていません。
終わりに
本ブログでは、未知反応を担う酵素の探索を実演しました。材料として論文で触媒する酵素を見つけたIslatravirの新規合成経路を用いました。この経路の各反応を担う酵素を類似反応酵素探索技術を用いて見つけることができるか試しました。5つの未知反応に対して、実際に類似反応をそれぞれ複数抽出しました。この際、任意のtaxonごとに配列を抽出し、それぞれの配列数を示しました。4つの反応では実際に論文で使っていた酵素を含む複数の配列を抽出することができました。そして、系統的位置を加味したスクリーニングで、全taxonから抽出した類似反応酵素を絞り込みました。通常のスクリーニングではさらに、酵素自体の性質(細胞局在など)や3次元構造など他の指標も使って候補配列を絞り込めます。
謝辞
今回の類似反応酵素探索には以下の論文のデータを利用させていただきました。
Huffman et al., (2019) Design of an in vitro biocatalytic cascade for the manufacture of islatravir. Science.
構造予測とMDシミュレーションを用いた酵素活性予測の実用例
はじめに
事業開発部の礒崎です。弊社では有用酵素探索の1つとして、分子動力学シミュレーションを用いた酵素活性予測を行っています。構造未知の酵素配列からその構造を予測し、標的化合物との複合体を分子動力学シミュレーションへ供します。その結果から、digzyme独自のスコアを算出し酵素活性を予測します。本ブログでは、その具体例としてthiolaseの1つoleAという酵素の類似配列から実際に活性をもつものを予測した結果をご紹介します。
酵素活性予測に使った材料
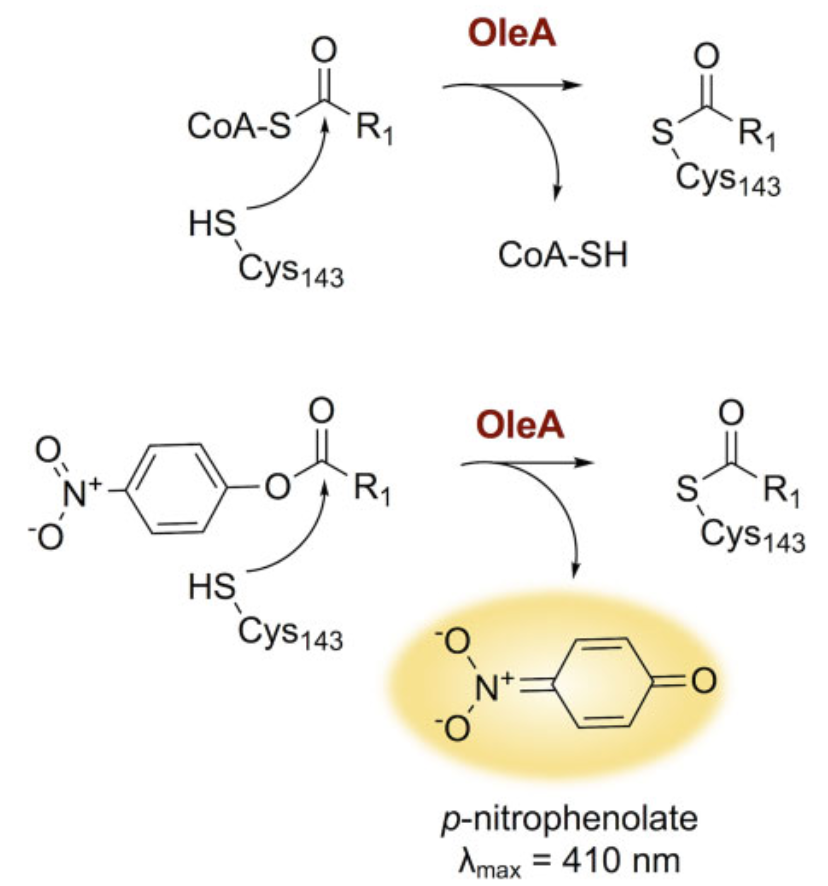
oleAの本来の基質はacyl-CoAです。このアシル基をoleAのCys143が脱離させます。この活性を調べる上で、p-nitrophenolateを用いた実験系が使われます(図1)。
結果
oleA類似配列59配列を対象にp-nitrophenolateの1種4-nitrophenyl-hexanoateを加水分解するか予測しました。
1.類似配列59配列の3次元構造予測
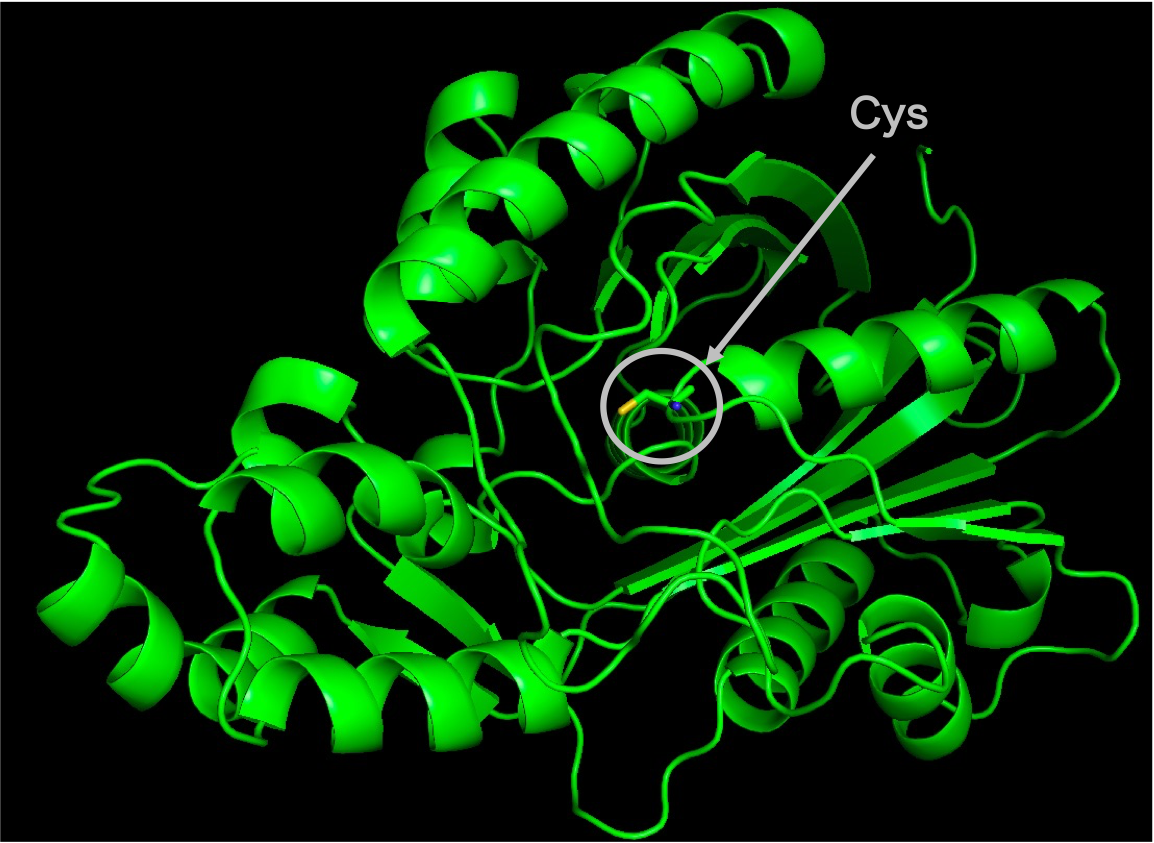
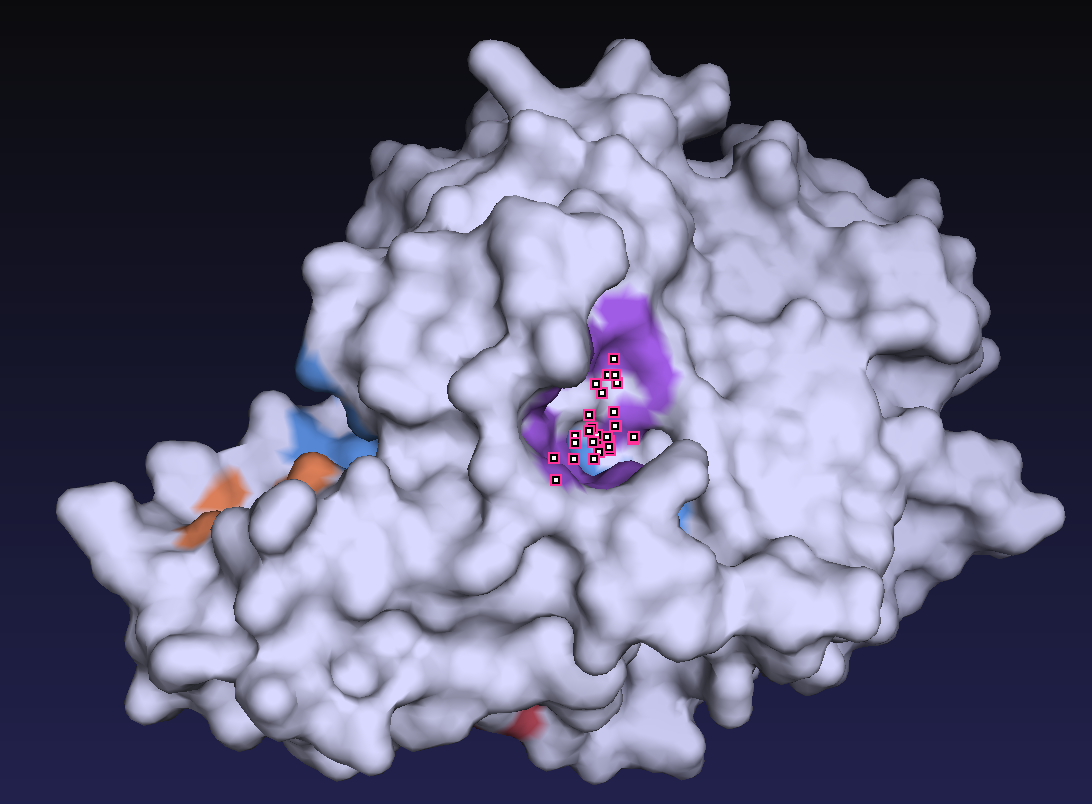
まずは類似配列59配列すべての構造が未知であるため、その3次元構造を予測し、予測した構造から活性残基の位置と基質が入るポケットの位置を予測しました。図2は類似配列の配列情報から予測した3次元構造および活性残基Cysの位置を示しています。図3が基質が結合するポケットの位置を予測した結果です。
2. 分子動力学シミュレーション
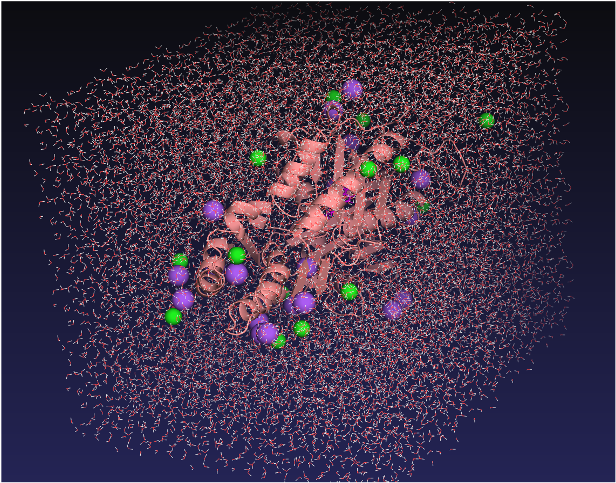
続いて、水分子とイオンの中に酵素と基質である4-nitrophenyl-hexanoateの複合体を配置して分子動力学シミュレーションを実行します(図4)。
3. digzyme独自酵素活性予測スコア算出
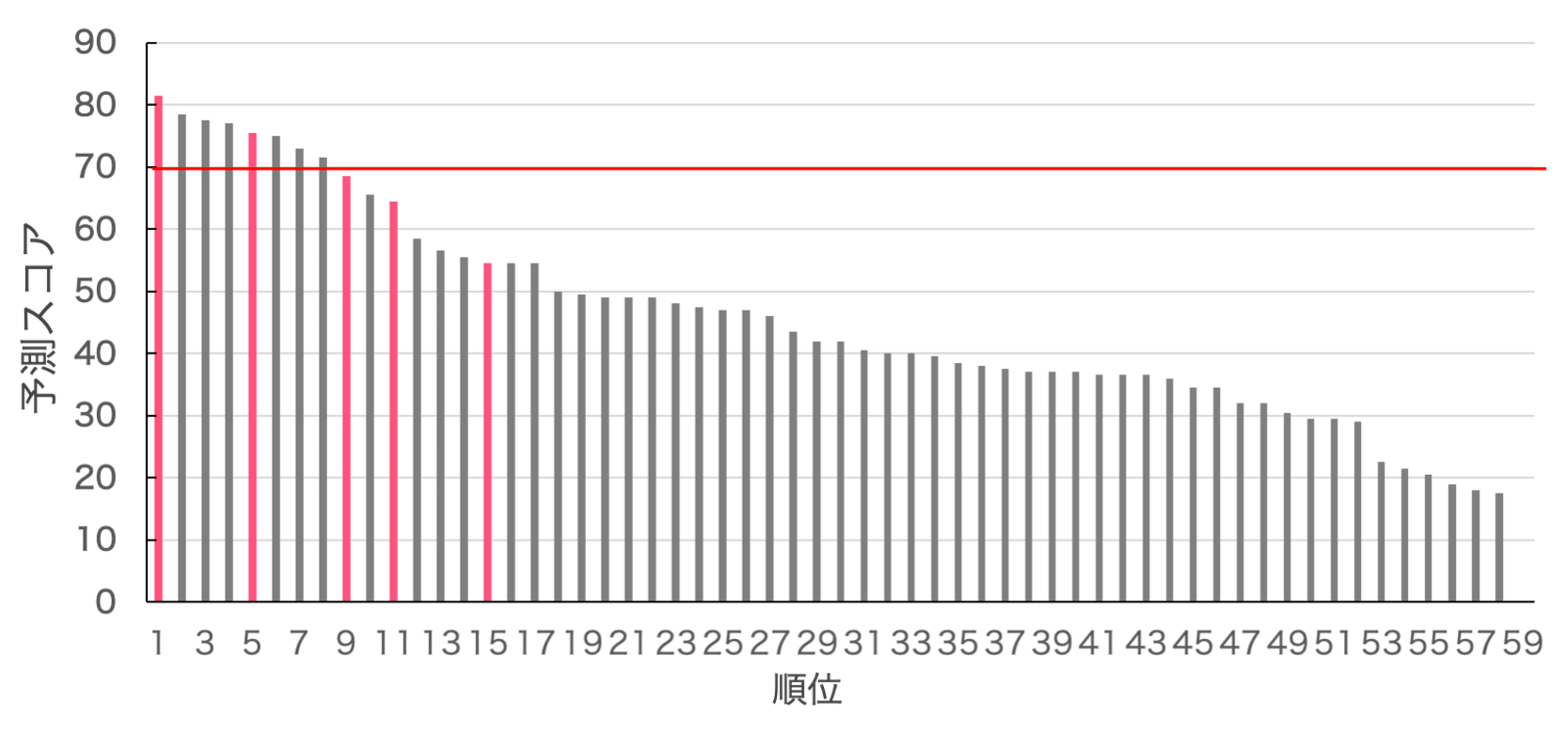
最後に分子動力学シミュレーションの結果から算出したdigzyme独自のスコアを計算します。図5にスコアが高い順に全59配列の予測スコアを記載しました。実証実験で活性があった配列をピンク色、活性がなかったものを灰色で表示しています。スコア70以上の配列を活性ありと判断しています(図5の赤線より上)。今回は9配列を活性ありと予測し、そのうち3配列が実際に活性を持っており、陽性適中率(PPV) = 0.30でした。また、真陽性率 (TPR) =0.6、偽陰性率 (FPR) =0.13という結果でした。このことから、不活性なものをランキング下位に分類できており、上位の配列に実際に活性のある配列を含んでいることが確認できました。
終わりに
本ブログでは、酵素活性予測技術を用いて、実験で活性が確認された酵素の活性予測を実演しました。通常実証実験を行う場合5~10配列を合成します。今回は上位5配列の中に実験で活性があった2配列が含まれており、弊社の酵素活性予測の精度が実用に適うものであると示されました。特に母集団の酵素配列のうち活性のあるものがわずかしか含まれていないようなケースを想定してデータを選びました(今回は59配列中5配列)。偽陰性率が低く抑えられているため、正しく酵素活性が予測できています。
謝辞
今回の酵素活性予測の材料として以下の論文から実証実験データを利用させていただきました。
Robinson et al., (2020) Machine learning-based prediction of activity and substrate specificity for OleA enzymes in the thiolase superfamily. Synthetic Biology.
